
ATAC-Seq测序平台
技术原理
ATAC-Seq(Assay for Transposase-Accessible Chromatin with high throughput sequencing)是一种创新的表观遗传学研究技术,该技术通过转座酶对某种特定时空下开放的核染色质区域进行切割,进而获得在该特定时空下基因组中所有活跃转录的调控序列。
在理解这个技术之前,需要先认识一下染色体的结构。
染色体主要由DNA和蛋白质组成,每一条染色单体由单个线性DNA分子组成,细胞核中的DNA是经过高度有序的包装,包装分为多个水平,核小体核心颗粒(nucleosome core particle)、染色小体(chromatosome)、 30nm水平染色质纤丝(30nm fibre)和高于30nm水平的染色体包装。
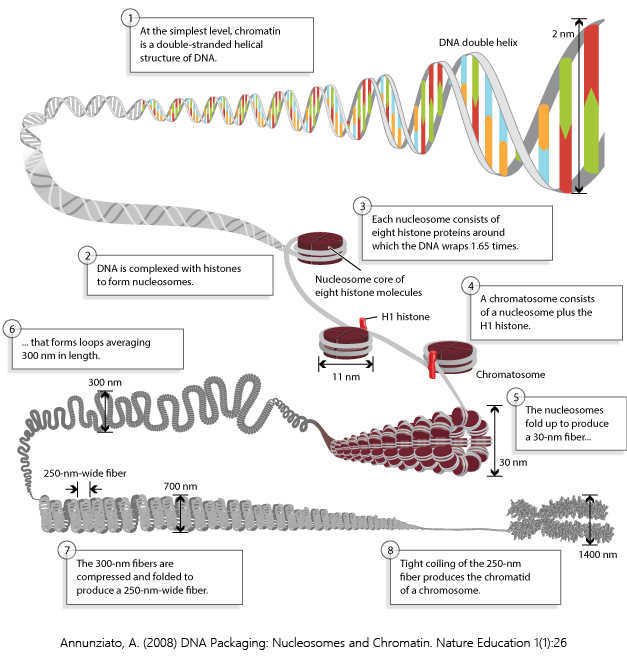
染色体的组成
DNA的复制,基因的转录,需要将DNA的高级结构解开,这部分打开的染色质,称为开放染色质(open chromatin),而打开的染色质,就允许一些调控蛋白(比如转录因子和辅因子)与之结合。染色质的这种特性,叫做染色质的可及性(chromatin accessibility)。
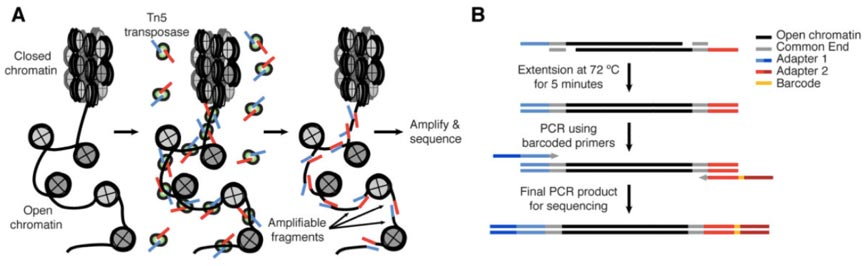
ATAC-seq技术原理
ATAC-seq利用Tn5转座酶(DNA转座,是一种把DNA序列从染色体的一个区域搬运到另外一个区域的现象,这一过程就由转座酶参与完成。Tn5转座酶:“标签片段化工具”,Tn5转座体可将其衔接子负载整合到可接近的染色质区域,而空间位阻较不可接近的染色质使得转座不可能发生。)人为将将携带已知DNA序列标签的转座复合物,加入到细胞核中,再利用已知序列的标签进行PCR建库测序,就知道哪些区域是开放染色质了。
技术流程

(*团队基于ATAC-seq发表Cancer Cell,Genome Biology,BIB等多篇高水平文章)
技术应用
l 重大疾病发病机制:癌症、生殖系统、糖尿病等疾病发病机制
l 药物相关研究:药物作用机制、新药研发、耐药性及敏感性研究
l 潜在标志物预测:临床生物标志物发现、生物标志物功能研究
l 染色体结构研究:染色体开发性图谱绘制、核小体定位预测、转录因子结合位点分析
技术优势
l 快速 — 实验流程精简,交付周期更短
l 微量 — 所需细胞量少,适用于临床样本
l 准确 — 技术重复性好,与同类技术及同类测序平台一致性高
l 全面 — 获得信息量大(全基因组调控活性图谱、全转录因子结合图谱)
送样要求
l 样本物种:人、大小鼠
l 样本类型:活细胞
l 细胞数量:50000
测序方案
l 测序模式:PE150
l 测序数据量:10-15 GB
l 测序深度:100 M以上,保证50 M 有效reads
参考案例
1. 药物靶点发现(*瀚因生命团队技术成果)
本⼯作中,利用ATAC-seq建立了10个正常⼈及14个CTCL病⼈服用共101个临床样本表观遗传数据。通过分析HDACi药物治疗前后差异,及不同疗效患者之间差异,建立CTCL癌症发病机制的表观遗传图谱,证明表观遗传状态对HDACi药物敏感性的决定性作用。
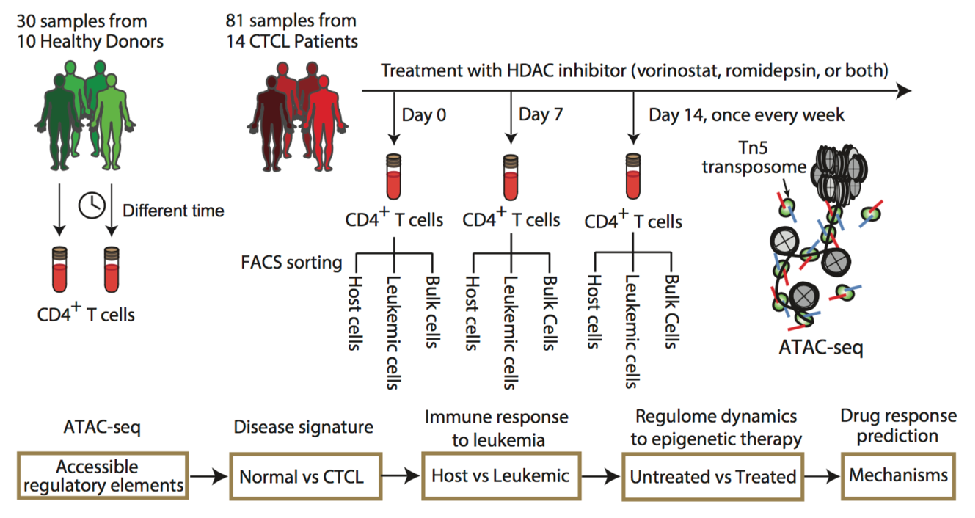
(K. Qu*, L. Zaba*, et al, H. Chang “Chromatin accessibility landscape of cutaneous T cell ymphoma and dynamic response to HDAC inhibitors”, Cancer Cell, 32:27-41, 2017)
2. ⼈体泛癌症表观遗传图谱
本⼯作中,利用ATAC-seq建立了23个主要癌种,共410例肿瘤样本的全景表观遗传状态图谱。建立了不同癌种之间差异及转移倾向的分⼦机制,以及DNA和表观遗传之间的相互作用。为新⼀代抗癌药和癌症早筛提供了数据支持。表明ATAC数据正式纳⼊TCGA数据库,成为国际公认的临床研究组学数据。
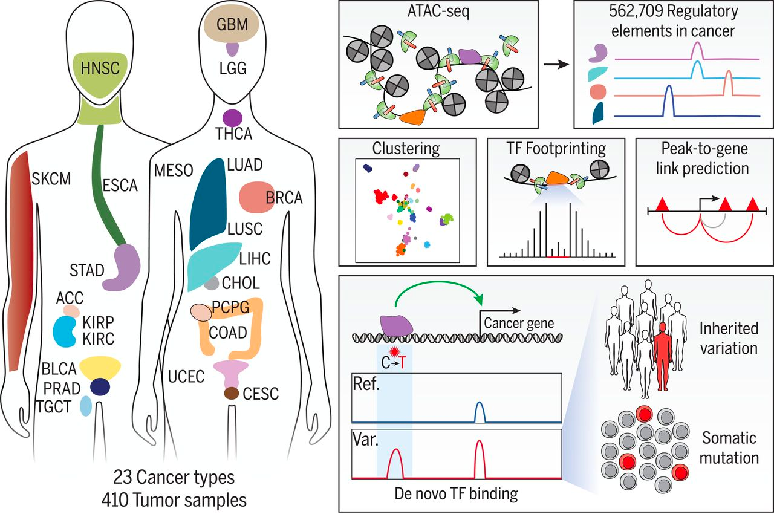
(Corces MR, Granja JM, Shams S, et al. The chromatin accessibility landscape of primary human cancers. Science 2018; 362: eaav1898.)
3. 重大疾病发病机制
该项目的研究课题为讨论人小细胞肺癌促进癌症扩散转移的背景机制。主要为比较原发性和肝转移性的小细胞肺癌细胞之间的差异。利用ATAC-seq,发现NFI家族转录因子富集在具有差异的染色质开放位点中,预示着NFI家族转录因子在调控肿瘤细胞转移中扮演着重要角色。在染色质高开放性位点区域伴随着Nfib拷贝数量增多,且Nfib在侵袭性原发性肿瘤和转移性肿瘤内高表达,Nfib表现出维持染色质及远端调控区域开放和促进神经基因表达的功能,说明了Nfib对促进癌细胞增殖和迁移具有重要的作用。
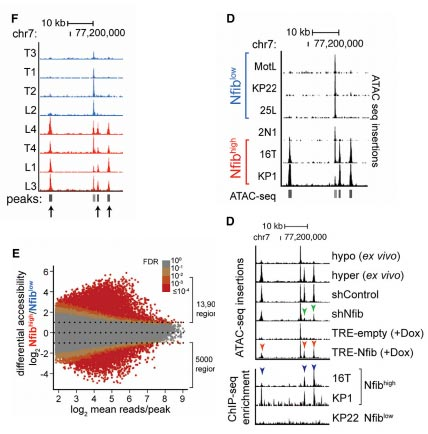
ATAC-seq与ChIP联合分析
(Sarah K. Denny,1,Dian Yang, et al.Nfib Promotes Metastasis through a Widespread Increase in Chromatin Accessibility. Cell ,2016, 166(2): 328–342. http://dx.doi.org/10.1016/j.cell.2016.05.052)
4. 分析转录因子作用机制
前列腺癌是全球范围内第二常见的癌症,仅2018年全世界就有约2000万新发病例和1000万死亡病例。转录因子FOXA1(forkhead box A1)在前列腺癌样本中高度突变或异常表达。然而,FOXA1对前列腺癌发生发展的具体作用机制迄今为止还未得到深入剖析。2019年,美国纪念斯隆·凯特琳癌症中心(Memorial Sloan Kettering Cancer Center)和威尔·康奈尔医学院(Weill Cornell Medicine)的多个课题组以及密西根大学的 Arul M. Chinnaiyan课题组背靠背在Nature发表了类似的研究结果,共同报道了关键转录因子FOXA1在促前列腺癌发生中的作用机制。由于FOXA1是一个先驱转录因子(pioneer tranion factor),可能具有在调控染色质可接近性方面的角色。为了探究FOXA1改变染色质可接近性影响前列腺癌细胞状态的可能性,作者对多个FOXA1过表达细胞系进行了ATAC-seq测序,结果发现野生型及两种FOXA1突变体均显著增加染色质开放位点。基于染色质位点开放程度的聚类分析指出野生型和突变型FOXA1在对具体位点的影响上有很大的差异,表明不同的突变位点对FOXA1的调控角色具有显著不同的影响。
FOXA1 mutations cause marked shifts in the chromatin landscape
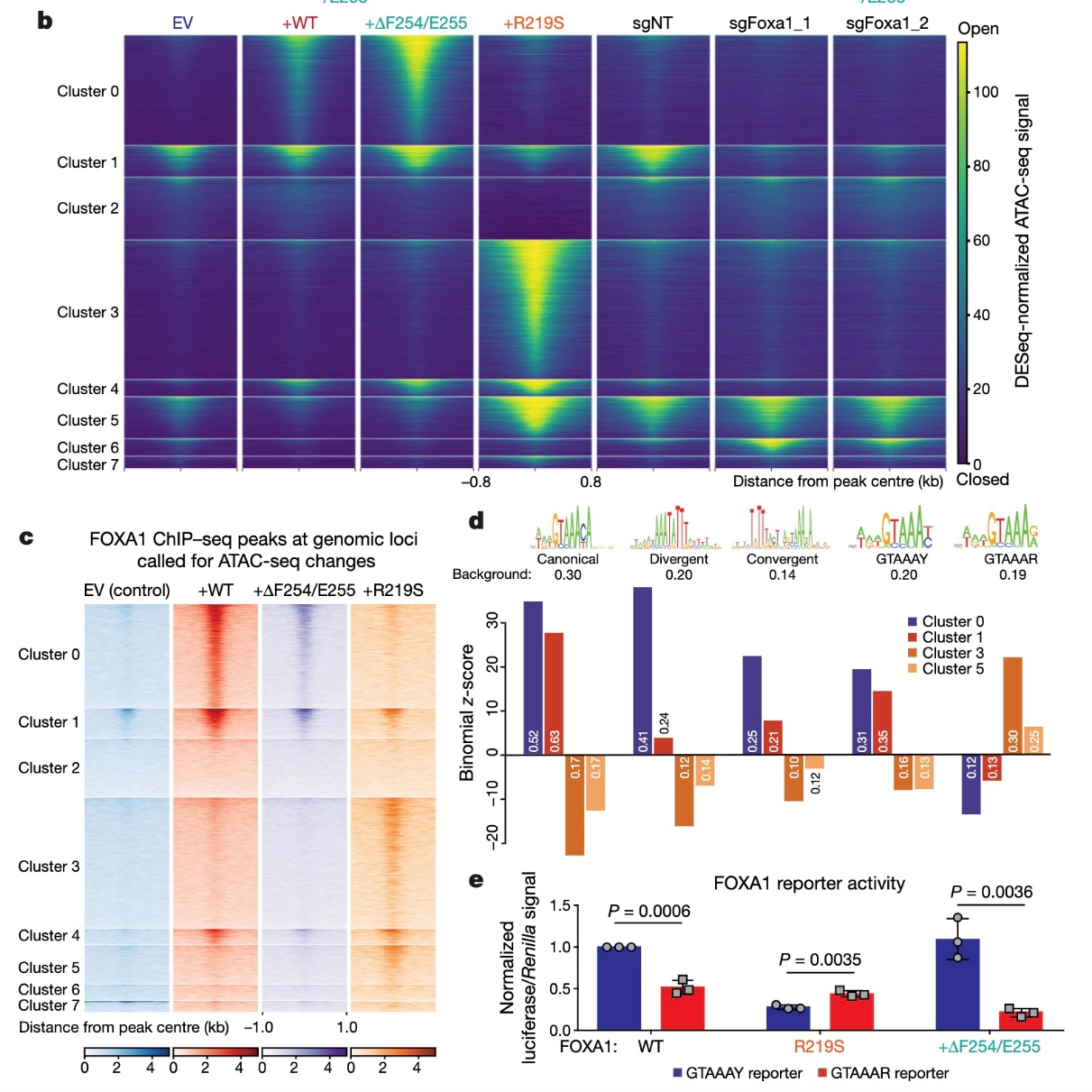
(Adams EJ, Karthaus WR, Hoover E, et al. FOXA1 mutations alter pioneering activity, differentiation and prostate cancer phenotypes. Nature 2019, 571(7765):408-412.)
ATAC-Seq生物信息分析
标准生信分析
1) 数据基本处理与质控


2) 文库插入片段长度分布
3) 基因组测序深度累积分布
4) 各样品基因promoter(up2K)区测序深度分布
5) 富集峰(peak)识别
利用流行的MACS软件进行峰识别,默认P < 10-5识别基因组上的ATAC富集峰。
6) 富集峰(peak)长度分布
根据ATAC-seq识别开放区域的DNA片段长度,对富集峰的Count数进行统计。
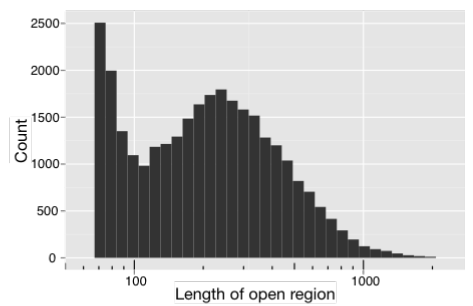
7) Peak深度分布
8) 样本生物学重复 IDR 分析
9) Peak在基因功能元件上的分布
根据注释信息,绘制富集峰在不同基因组特征上的比例图。
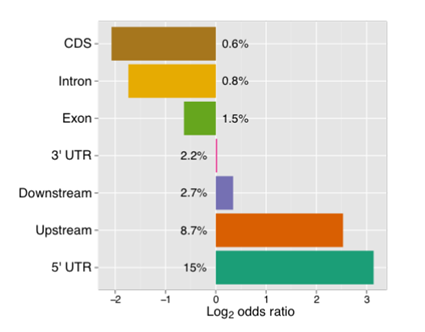
10) Peak相关基因
11) Peak相关基因的GO功能显著性富集分析
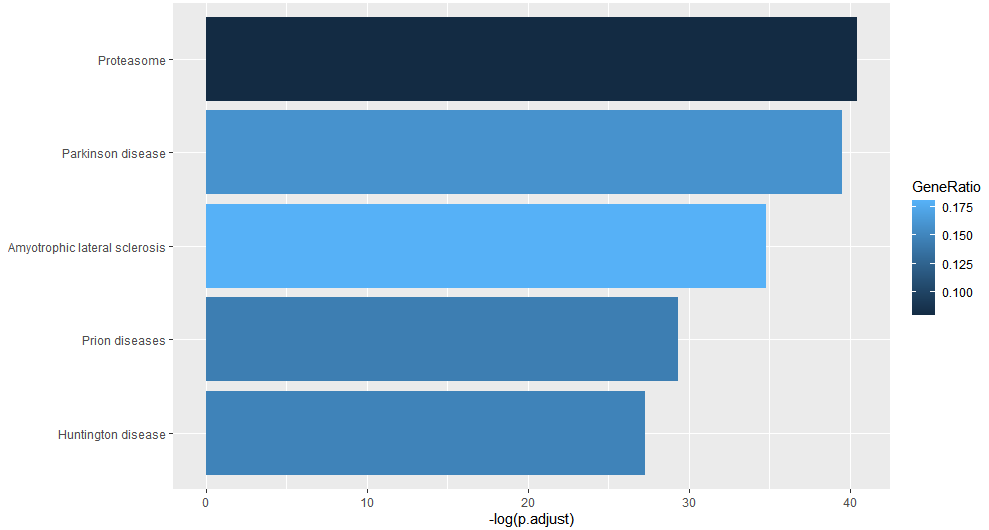
12) Peak相关基因的pathway富集分析
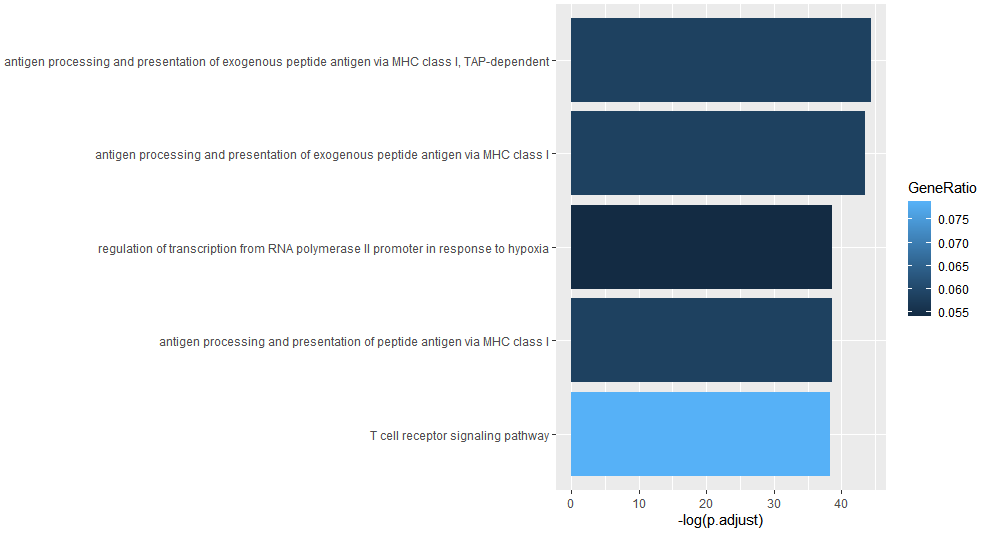
13) 样本间差异peak检测
使用DESeq包进行样本间差异peak的识别。默认筛选标准为FDR<=0.05,具体以报告为准。
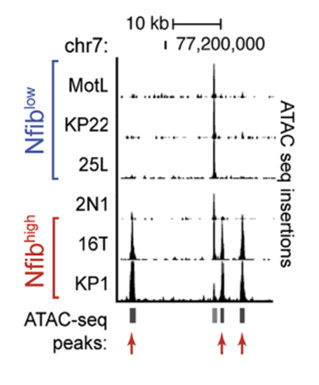
14) 样品间差异peak在基因功能元件的分布
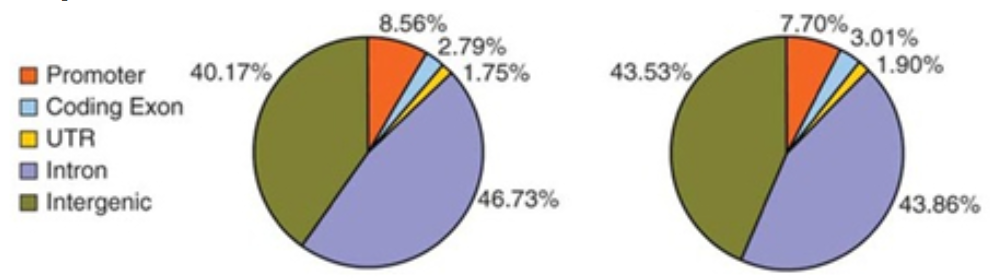
15) 样品间差异peak列表及显著性

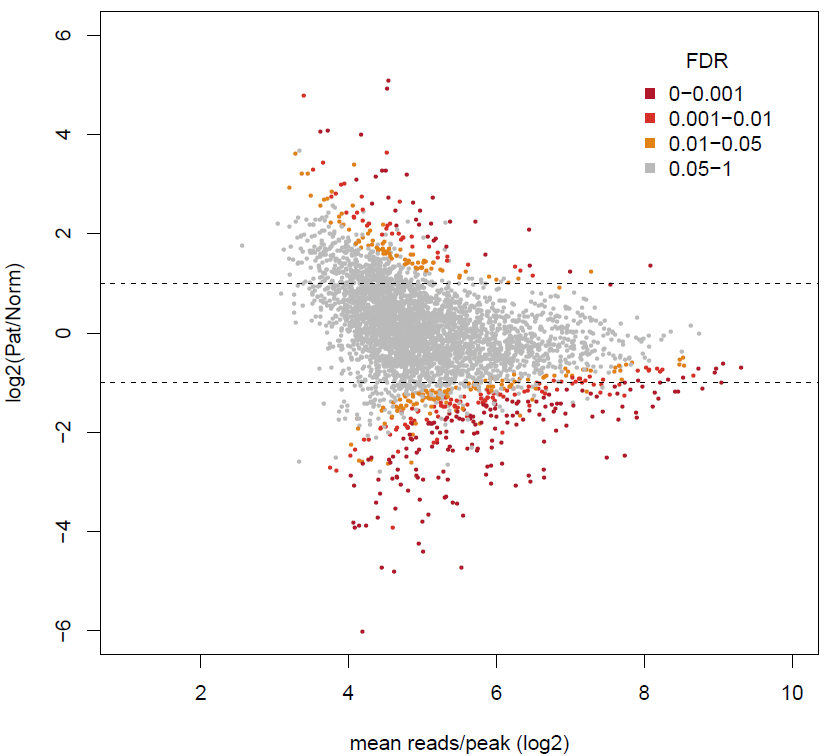
16) 样品间差异peak相关基因的GO和KEGG富集分析
对差异peak相关基因进行功能分类,并发现明显富集的功能条目。

17)样本间count相关性
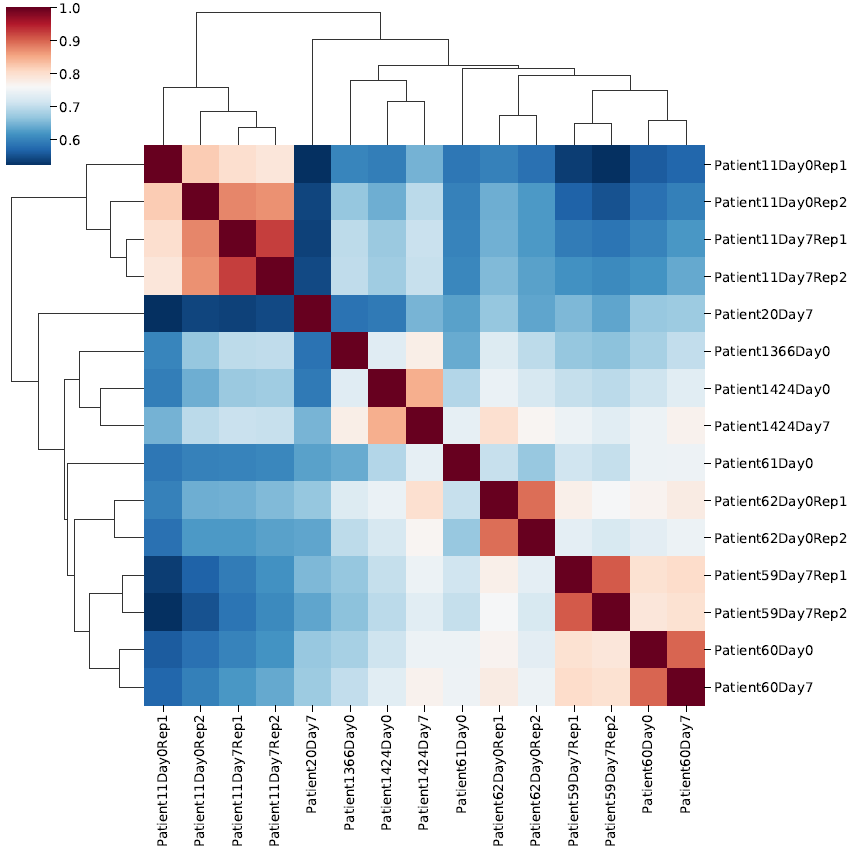
高级生信分析:
18) 核小体定位分析
由DNA和组蛋白形成的核小体是构成真核细胞染色质的基本结构单位,每个核小体由146bp的DNA缠绕组蛋白八聚体约1.65圈形成,核小体与核小体之间通过20-50bp的连接DNA相连,DNA与组蛋白的结合并不是固定不变的,没有核小体结合的DNA区域易于各种调节蛋白的接近和结合。在基因组上核小体位置的精确确定称为核小体定位,它的定位变化总是伴随着基因从抑制到转录状态的转变,核小体定位在转录调控、DNA复制和修复等多种细胞过程中有重要研究价值,也是目前表观遗传学研究的热点。结合核小体结构特征和ATAC-Seq插入片段分布进行分析,将插入片段105bp以内的片段判定为NFR区域(核小体缺失区域),将105-250bp插入片段判定为核小体分布区域,进而对核小体进行精准定位。

核小体结构结构
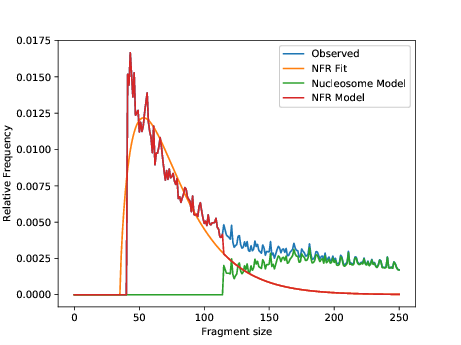
核小体定位预测模型
19) 转录因子结合分析(需客户提供感兴趣的TF名称)
真核生物基因表达是一个复杂而有序的过程,它是众多反式作用因子和顺式作用元件之间相互作用的结果,特定时间空间下又有哪些反式作用因子和顺式作用元件互作参与?
反式作用因子是指能直接或间接识别和结合在顺式作用元件上,调控靶基因表达的蛋白质因子,一般也称为转录因子(transcriptional factor,TF),转录因子结合位点((Transcription factor binding site, TFBS)是与转录因子结合的DNA 序列。确定TFBS是理解转录调控机制, 建立转录调控网络的关键问题。通过ATAC-Seq转录因子足迹分析(TF footprinting analysis), 可对TF结合情况进行预测,甚至进一步对全转录因子结合进行分析。

转录因子结合预测模型
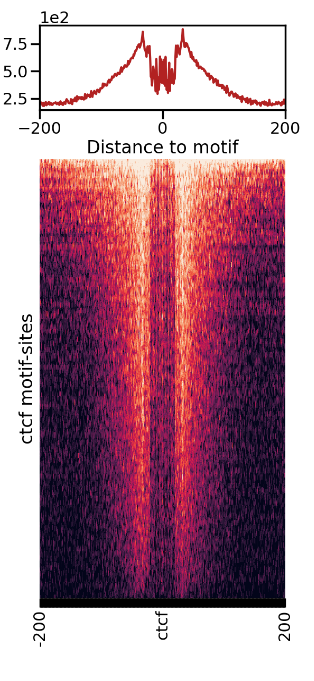
ctcf结合印记
20) 调控网络图谱
许多转录因子充当着主调节因子和选择基因的角色,控制着细胞类型的决定、发育模式和特定途径(如免疫反应)的过程。转录因子和转录因子结合位点突变是人类致病的主要因素。确定转录因子如何以不同方式组装以识别绑定位点和调控"网络"转录是一项庞大的工作,但是,对于理解它们的生理作用、解码基因组的特定功能,以及在复杂生物中绘制高度特异性表达程序的编排是至关重要的。根据客户感兴趣的TFs,确定其调控网络关系。

正常和患者个体之间CD4+T细胞转录因子调控网络
21) 全基因组活性图谱
染色质结构的改变对细胞的命运会产生极大的影响,染色质结构开放程度影响蛋白结合程度,开放程度也直接反映了染色质转录活性,因此,对特定时间空间下染色质开放区域进行捕获,获得全基因组调控活性区域信息,对基因表达调控网络研究具有重要意义。
通过 ATAC-Seq数据分析,可以获得高置信度的染色体结构开放区域。结合reads分布和 Peak检测结果,绘制出每个样品在整个基因组水平上的调控活性图谱。

全基因组调控活性图谱
更多定制化信息分析…
可结合客户的需求,协商确定定制化信息分析内容(如ATAC-Seq与RNA-Seq关联分析等)。
关于
瀚因生命
瀚海寻因,生命启航
致力于eccDNA新模态临床测序技术及临检产品开发
瀚因生命团队具有丰富的临床组学测序技术、及生物信息学算法开发经验,相关研究发表在Nature, Cell, Nature Methods,Cancer Cell,GenomeBiology等高水平学术期刊。团队自2020年五月成立以来,已建立合肥实验中心和杭州生信中心双平台,全力打造围绕eccDNA血液检测的泛癌早筛/伴随诊断/预后跟踪等肿瘤全周期产品管线。

扫码关注官方公众号

扫码关注环环测公众号

扫码进入环环测小程序

环环测咨询电话:400-007-5070
合作电话:15958809922
地址:浙江省杭州市萧山区萧山科技城传化科创大厦A座701-B
上一篇:ctDNA甲基化
下一篇:none